Un equipo internacional de investigadores logró generar las primeras secuencias genómicas completas, sin brechas, de seis variedades de maní. El avance entrega una referencia genética de alta resolución para estudiar la evolución del cultivo y apoyar futuras estrategias de mejoramiento genético orientadas a características como tamaño de semilla, rendimiento y calidad de aceite.
ChileBio / 2 de mayo, 2026.- Un equipo internacional obtuvo genomas completos, de telómero a telómero, de seis variedades de maní y analizó 521 accesiones de todo el mundo. El trabajo permitió identificar genes candidatos asociados al contenido de aceite y al tamaño de semilla, información que podría acelerar programas de mejoramiento convencional asistido por marcadores moleculares.
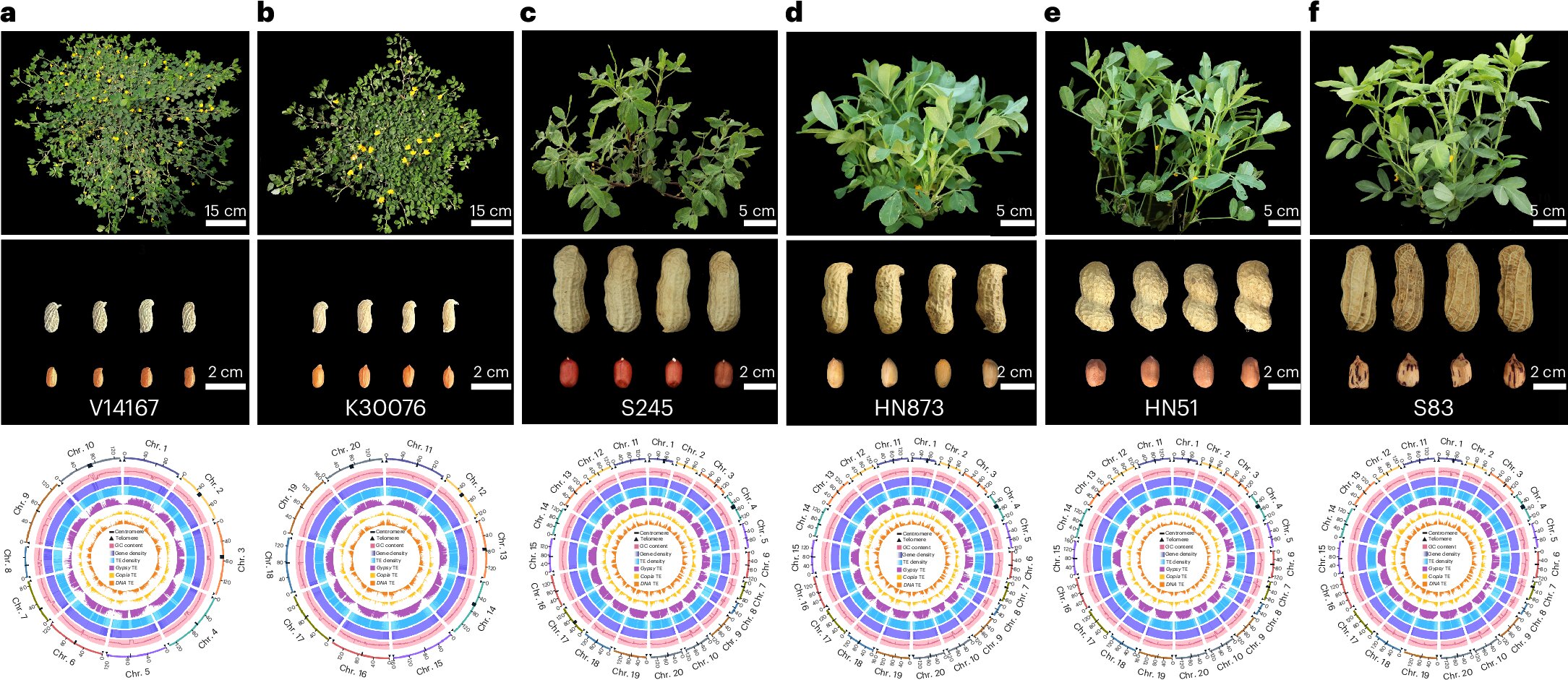
El trabajo, publicado en Nature Genetics, fue desarrollado por investigadores de Murdoch University, Peking University Institute of Agricultural Sciences, Guangxi Provincial Academy of Agricultural Sciences, Shandong Academy of Agricultural Sciences y Zhejiang University. El estudio incluyó dos especies silvestres ancestrales del maní cultivado, cuatro variedades cultivadas y el desarrollo de genomas de referencia para dos subespecies de maní que no habían sido completamente mapeadas.
El maní es una leguminosa de importancia global, valorada como fuente de proteína vegetal y aceite comestible. Sin embargo, su genoma ha sido históricamente difícil de estudiar debido a su estructura compleja y a la abundancia de regiones repetitivas. Según el comunicado de Murdoch University, estos desafíos habían dejado zonas sin mapear en estudios previos, limitando el uso de herramientas modernas de genómica aplicada al mejoramiento vegetal.
[Recomendado: Nuevo “pangenoma” del maní revela la clave genética para aumentar su rendimiento agrícola]
El profesor Rajeev Varshney, director del Centre for Crop and Food Innovation de Murdoch University y coautor correspondiente del estudio, explicó que el maní es una fuente básica de aceite comestible y proteína para cientos de millones de personas, pero que su genética ha sido más difícil de trabajar que la de la mayoría de los principales cultivos. Con este nuevo recurso, señaló, los investigadores y mejoradores cuentan finalmente con “un genoma de referencia sin brechas” para avanzar hacia variedades de mayor rendimiento y valor nutricional.
Para construir esta base genómica, los investigadores generaron ensamblajes de tipo “telómero a telómero” —conocidos como T2T—, una estrategia que permite reconstruir los cromosomas desde un extremo hasta el otro. En términos simples, esto equivale a contar con un mapa mucho más completo del ADN del cultivo, incluyendo regiones que antes quedaban ocultas o incompletas.
Además, el equipo analizó el ADN de 521 accesiones de maní recolectadas en distintas regiones del mundo. Con esta información buscaron variantes genéticas asociadas a rasgos de interés agronómico, como tamaño de semilla, contenido de aceite y otros atributos relevantes para la producción agrícola.
Uno de los hallazgos centrales fue la identificación del gen AhWRI1, asociado al contenido de aceite en la semilla. De acuerdo con el comunicado, distintas versiones de este gen se relacionaron con diferencias cercanas a seis puntos porcentuales en contenido de aceite, con valores aproximados de 48% frente a 54% entre los grupos analizados.
El estudio también identificó el gen AhGSA1, asociado al tamaño y peso de la semilla. Las líneas de maní que portaban una versión específica de este gen alcanzaron en promedio alrededor de 846 gramos por mil semillas, en comparación con 491 gramos en líneas con la versión alternativa, una diferencia superior al 70%.
[Recomendado: Un maní editado genéticamente libre de alérgenos se prepara para llegar al mercado de EE.UU.]
Estos genes no implican, por sí mismos, el desarrollo de una nueva variedad transgénica o editada genéticamente de maní. El comunicado destaca que ambas variantes podrían utilizarse como marcadores de ADN en programas de mejoramiento convencional, acelerando la selección de variedades con mayor rendimiento o contenido de aceite.
El estudio también entregó nueva información sobre la evolución del maní cultivado. Esta especie posee dos conjuntos de cromosomas provenientes de especies ancestrales distintas que se fusionaron hace miles de años. Varshney señaló que, si bien esto ya era conocido, el equipo no había dimensionado cuán asimétrica había sido la evolución de ambos componentes del genoma. Comprender esa divergencia, agregó, ayuda a explicar el comportamiento genético del maní y a identificar dónde podría encontrarse la diversidad útil para el mejoramiento.
El profesor Peter Davies, Pro Vice Chancellor del Food Futures Institute de Murdoch University, destacó la relevancia agrícola y alimentaria del cultivo. Según Davies, el maní cumple un papel importante en seguridad alimentaria y nutrición, y sus propiedades de fijación de nitrógeno lo convierten en una buena opción para rotaciones agrícolas más sostenibles.
Por su parte, el profesor Peter Eastwood, Deputy Vice Chancellor Research & Innovation de Murdoch University, subrayó la magnitud técnica del avance. Recordó que el primer ensamblaje T2T del genoma humano se logró hace solo cuatro años y afirmó que obtener ensamblajes T2T de seis variedades de maní, un cultivo con cuatro juegos de cromosomas provenientes de dos especies, representa un logro notable.
Para los investigadores, esta información permite entender mejor la domesticación del maní y localizar con mayor precisión la diversidad genética útil para el mejoramiento. En la práctica, contar con genomas completos puede ayudar a los programas de breeding a desarrollar variedades con mejor desempeño productivo, mejor composición de aceite y características agronómicas adaptadas a distintas condiciones ambientales.
Este avance se suma a una tendencia creciente en agricultura: el uso de herramientas genómicas de alta precisión para acelerar el mejoramiento de cultivos. A diferencia de enfoques basados en prueba y error, la genómica permite identificar variantes naturales asociadas a rasgos de interés y utilizarlas de manera más eficiente en programas de selección.
- Fuente: Murdoch University News — First gap-free peanut genomes reveal genes behind bigger seeds and better oils. Publicada el 24 de abril de 2026.
- Estudio: Bian, J. et al. Telomere-to-telomere genome assemblies and population resequencing of diploid and allotetraploid peanut varieties. Nature Genetics, publicado el 24 de abril de 2026. DOI: 10.1038/s41588-026-02577-z

