
Un equipo internacional de científicos identificó millones de secuencias reguladoras conservadas en plantas, algunas con una antigüedad de hasta 300 millones de años, revelando que gran parte del control de la actividad genética vegetal tiene raíces evolutivas mucho más profundas de lo que se pensaba. El hallazgo podría mejorar la precisión de la edición genética y abrir nuevas posibilidades para desarrollar cultivos más productivos y resilientes.
ChileBio / 12 de marzo, 2026.- Durante años, los científicos pensaron que en las plantas era muy difícil encontrar secuencias regulatorias antiguas conservadas a lo largo de la evolución. Ahora, una investigación internacional publicada en Science muestra que esas secuencias sí existen, son abundantes y han permanecido activas durante cientos de millones de años.
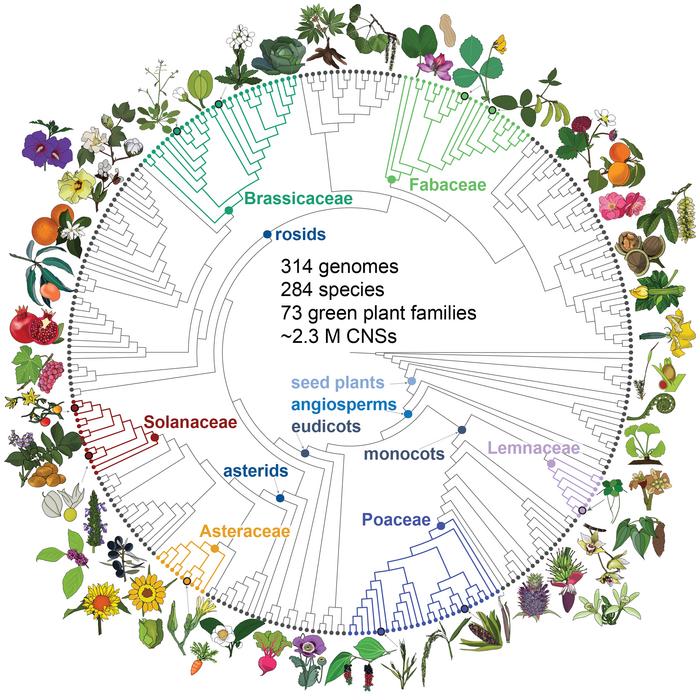
El estudio identificó cerca de 2,3 millones de secuencias no codificantes conservadas en 284 especies de plantas pertenecientes a 72 familias, incluyendo monocotiledóneas, eudicotiledóneas, gimnospermas y algas. Muchas de estas regiones del ADN no producen proteínas, pero cumplen una función clave: actúan como elementos reguladores que controlan cuándo, dónde y en qué nivel se activan los genes.
Los investigadores hallaron incluso más de 3.000 secuencias regulatorias que anteceden a la aparición de las plantas con flor, y algunas se remontan a unos 300 millones de años. Esto sugiere que parte importante de los programas genéticos que gobiernan el desarrollo vegetal se estableció hace muchísimo tiempo y se ha mantenido, a pesar de los grandes cambios que han experimentado los genomas de las plantas.
[Recomendado: El sorprendente truco evolutivo de las plantas: transferencia de genes entre especies distintas al descubierto]
Uno de los aspectos más llamativos del trabajo es que estas secuencias ancestrales han logrado persistir pese a la complejidad de los genomas vegetales. A diferencia de muchos animales, las plantas han pasado repetidamente por duplicaciones completas del genoma, pérdida de genes y reordenamientos cromosómicos. Todo eso hacía muy difícil seguir el rastro evolutivo de las regiones regulatorias.
Para superar ese problema, el equipo desarrolló una nueva plataforma de genómica comparativa llamada Conservatory, diseñada para detectar secuencias regulatorias conservadas incluso cuando los genomas han cambiado mucho con el tiempo. El método combina relaciones de microsintenia, alineamientos graduales y un muestreo filogenómico profundo, permitiendo reconstruir conexiones entre genes y sus regiones reguladoras que antes pasaban desapercibidas.
Los resultados muestran que estas secuencias reguladoras antiguas se concentran especialmente cerca de genes vinculados al desarrollo vegetal, entre ellos varios factores de transcripción fundamentales. En otras palabras, muchas de las instrucciones que organizan procesos como la formación de meristemos, hojas, flores o tejidos epidérmicos dependen de elementos regulatorios con una historia evolutiva extraordinariamente antigua.
El estudio también analizó elementos reguladores conocidos asociados a ocho factores de transcripción implicados en el desarrollo. En todos los casos, esos elementos funcionales coincidieron con secuencias antiguas detectadas por Conservatory. Uno de los ejemplos más destacados fue el promotor de WUSCHEL, un gen central para el mantenimiento de células madre vegetales, donde se encontraron elementos conservados durante unos 300 millones de años.
Sin embargo, estas secuencias no son fósiles inmóviles. La investigación sugiere que pueden desplazarse, duplicarse y diversificarse con el tiempo, mientras conservan la lógica regulatoria necesaria para controlar el desarrollo. Esto muestra que la evolución del ADN regulador combina estabilidad funcional con flexibilidad estructural.
Otro hallazgo relevante es que los elementos regulatorios no siempre se ubican cerca de los genes que controlan. Aproximadamente una cuarta parte de las secuencias conservadas identificadas estaba a más de 25 kilobases de distancia de su gen objetivo, e incluso algunas parecían “saltar” genes vecinos. Esto pone en cuestión enfoques experimentales tradicionales que asumen que las regiones regulatorias importantes están siempre en las inmediaciones del gen estudiado.
[Recomendado: PubPlant: el «Google Maps» del ADN de las plantas que promete revolucionar la genómica vegetal]
Además, el trabajo mostró que muchas secuencias regulatorias nuevas aparecen después de eventos de duplicación génica. En varios casos, una copia del gen conserva los elementos regulatorios ancestrales, mientras la otra adquiere nuevas regiones reguladoras. Ese proceso puede ayudar a explicar cómo evolucionan nuevas formas y funciones en las plantas. En ciertos linajes, como las gramíneas, esta reorganización regulatoria habría sido particularmente intensa en etapas tempranas de su evolución.
Más allá de su valor evolutivo, el hallazgo tiene implicancias prácticas. La mejora genética vegetal y la edición genómica están avanzando rápidamente, pero uno de los grandes desafíos es saber qué secuencias conviene modificar para obtener cambios predecibles y beneficiosos. Este mapa de ADN regulador conservado puede transformarse en una guía para intervenir genes con mayor precisión, afinando rasgos de interés agronómico como rendimiento, desarrollo, adaptación o resiliencia.
En vez de limitarse a eliminar genes o duplicarlos, la tendencia en biotecnología vegetal es intervenir las regiones que regulan su expresión. Ese cambio de enfoque permite ajustar con más sutileza la actividad genética. En ese contexto, identificar secuencias regulatorias que han resistido cientos de millones de años de evolución ofrece una pista valiosa sobre cuáles son realmente cruciales para el funcionamiento de la planta.
La investigación fue liderada por equipos de la Universidad de Cambridge, la Universidad Hebrea de Jerusalén y Cold Spring Harbor Laboratory. El artículo, titulado “A deep-time landscape of plant cis-regulatory sequence evolution”, fue publicado en Science el 12 de marzo de 2026.

